组学数据
单细胞ATAC测序分析
Characterize chromatin accessibility changes underlying cell state transitions
在此用例中,我们再现了研究“HOX13依赖的染色质可及性揭示了向指状结构发育程序过渡的基础”的一部分分析(Desanlis et al., 2020, Nature Communications),以展示Drylab如何复制已发表的计算流程。
目标:
从近端到远端肢体身份的过渡和指状结构的形成需要精确的染色质重塑。HOX13蛋白(HOXA13和HOXD13)被认为对指状结构发育至关重要,但其在染色质层面的确切作用仍未完全理解。
数据集:
此重新分析使用公共scATAC-seq数据集GSE145657(Desanlis et al., Nat Commun (2020))提供了一种全面、可重复的鼠胚胎前肢芽中HOX13依赖的染色质可及性变化的视角。
质控过滤:
选择了标准阈值,保留了5,581个WT和3,856个KO细胞,中位FRIP约为0.92,表明高文库质量。
阈值 | 保留细胞 |
|---|---|
宽松 (log10TN >= 2.5, SE >= 50, FRIP >= 0.60) | 10,072 (76.5%) |
标准 (log10TN >= 3.0, SE >= 100, FRIP >= 0.70) | 9,437 (71.6%) |
严格 (log10TN >= 3.5, SE >= 200, FRIP >= 0.75) | 9,019 (68.5%) |
降维:
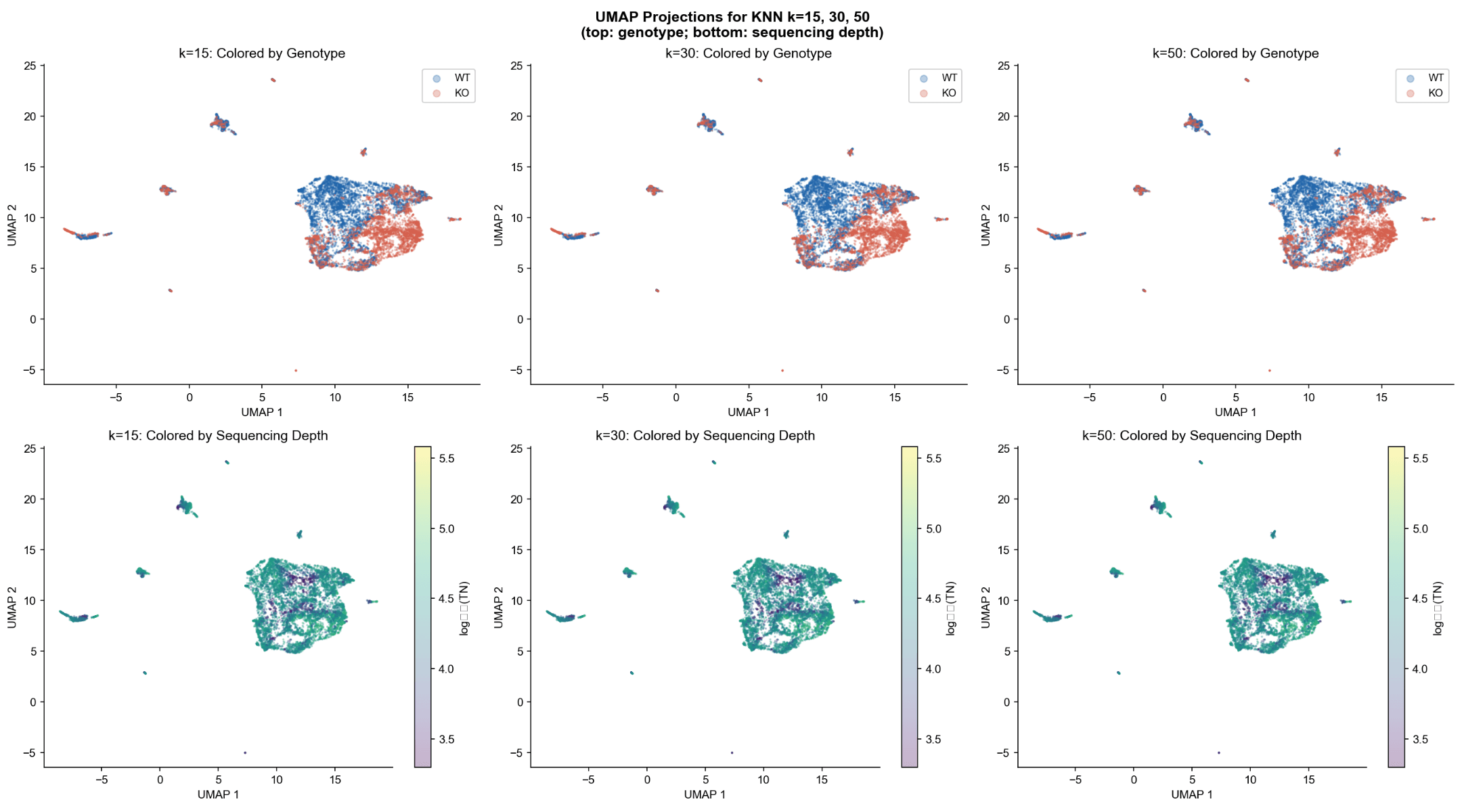
- 光谱嵌入产生了46个非平庸成分;肘部检测将主导的生物信号定位在成分5上。
- 在k = 15, 30, 50时UMAP拓扑结构稳定,证实流形结构的稳健性。
参数集 | n_clusters | 轮廓值 | 子采样ARI |
|---|---|---|---|
k=15, res=1.0 | 19 | 0.136 | 0.724 +/- 0.059 |
k=30, res=1.0 | 17 | 0.144 | 0.776 +/- 0.042 |
k=50, res=0.6 | 12 | 0.172 | 0.802 +/- 0.074 |
聚类稳定性网格搜索
最佳参数(k = 50, 分辨率 = 0.6)同时实现了最高的轮廓得分和子采样ARI,产生12个簇。
聚类稳定性网格搜索
最佳参数(k = 50, 分辨率 = 0.6)同时实现了最高的轮廓得分和子采样ARI,产生12个簇。
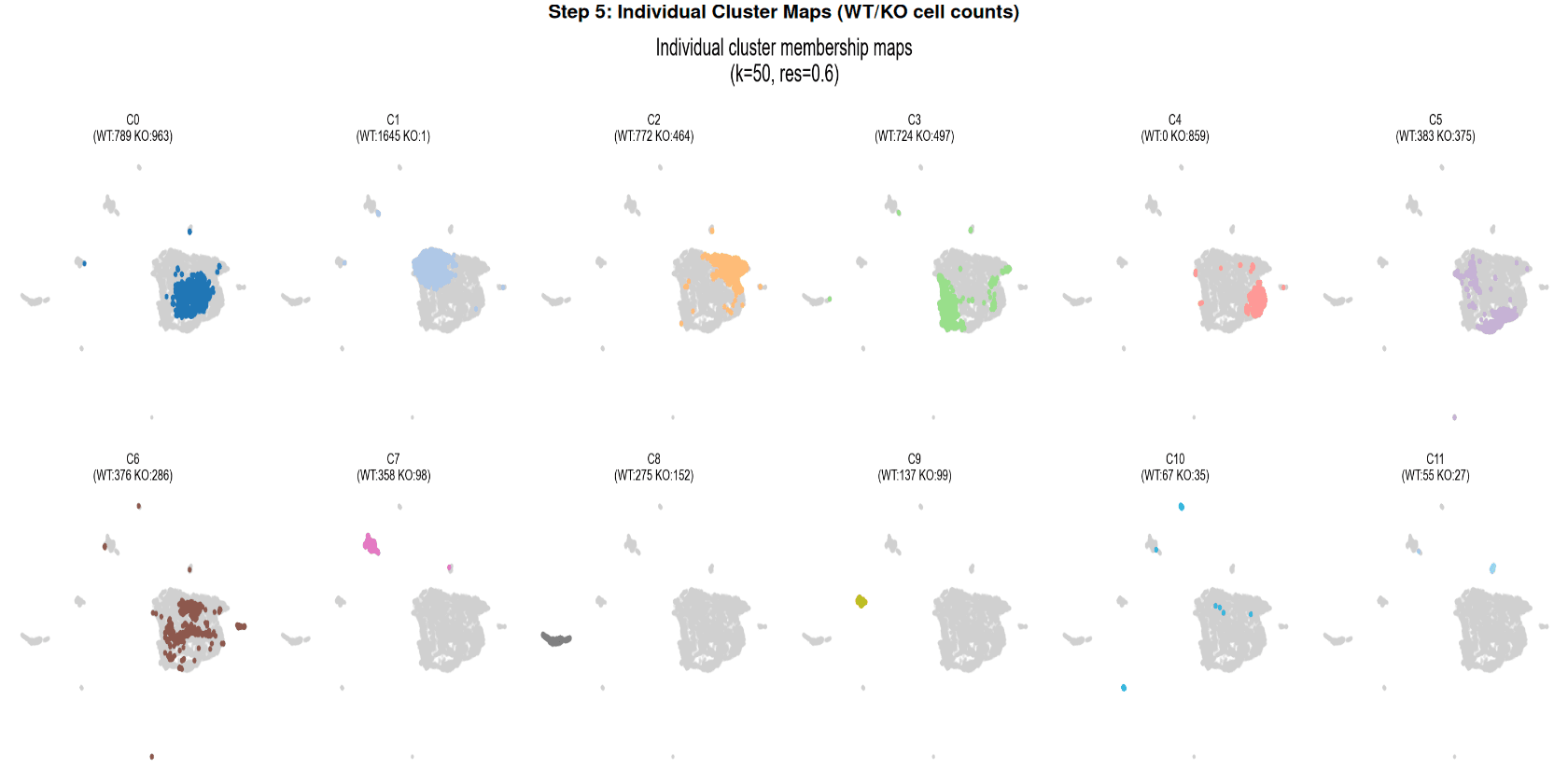
- WT和KO细胞占据很大程度上重叠的区域,但具有明显的基因型偏向亚群。
- 测序深度分布均匀,不推动观察到的分离,证实生物学(而非技术)差异。
- 流形结构稳定,基因分离不是文库质量的假象。
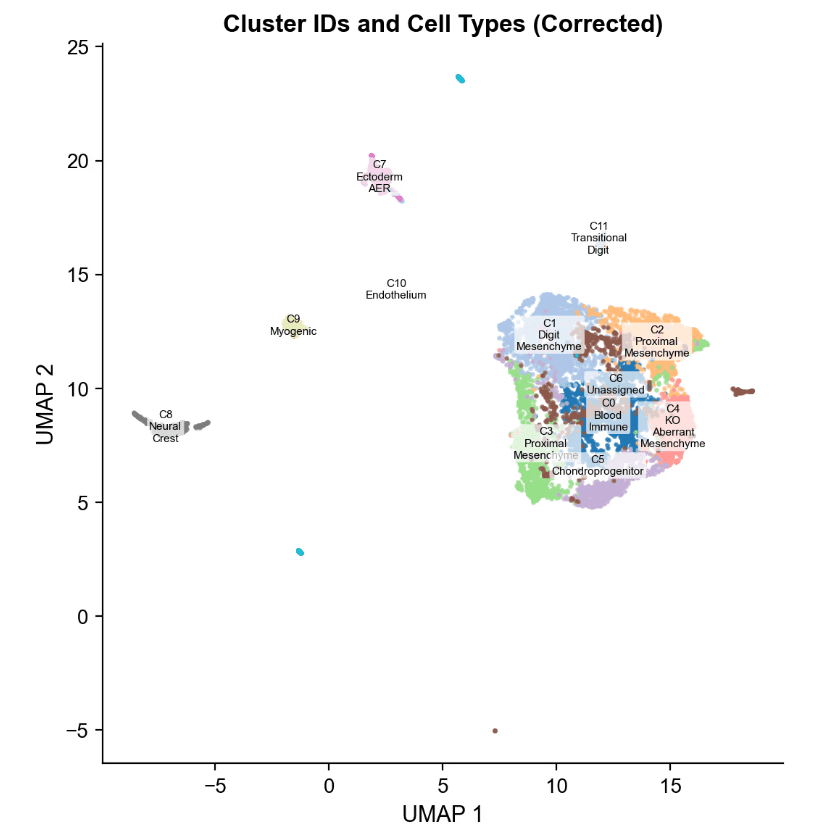
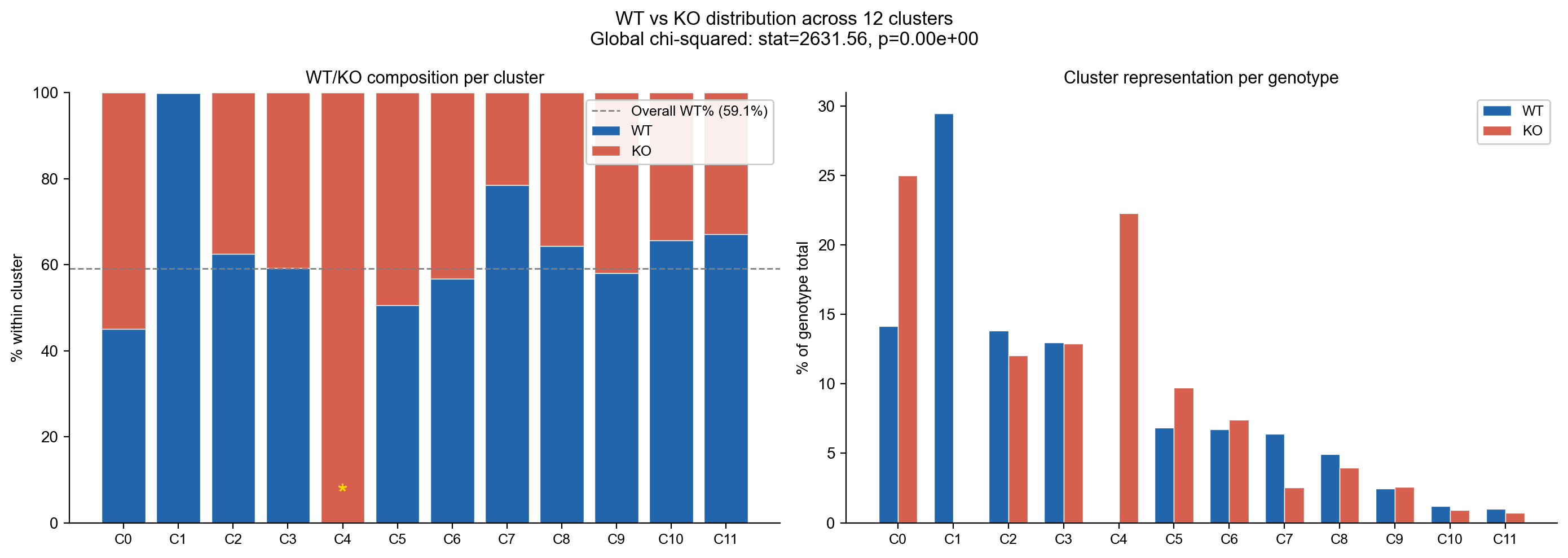
12个簇中的基因型分布
全局χ²检验(统计量 = 2,631.56, p ≈ 0)显示基因型和簇之间存在显著关联。
每个簇的WT/KO组成(左)及其对簇的贡献(右)。
- C1(指间质):1,646个细胞,99.9 % WT
- C4(KO-异常间质):859个细胞,100 % KO
其他大多数簇是共享的,HOX13仅影响特定细胞状态。
统计富集 – 森林图
每簇Fisher精确检验,BH校正和引导法95% CI。
- C1极度富集于WT(log2 OR +10.07)。
- C4完全排除KO(log2 OR −11.64)。灰条表示独立于HOX13的簇。
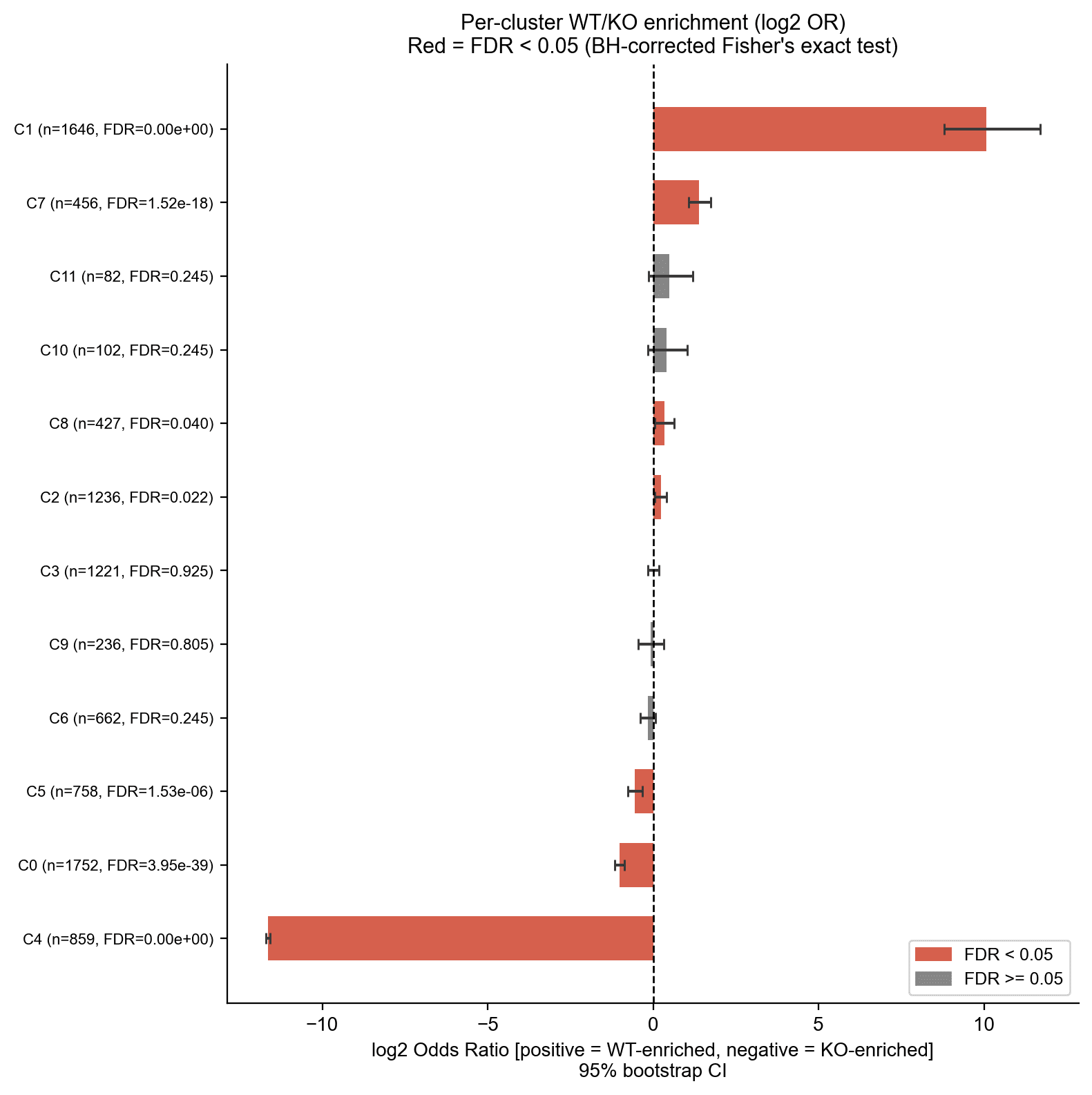
这与原研究的远端特定簇(簇2和6)一致,这些簇富含HOXA13基序且与指形态发生基因本体条款相关,而在Hox13-/-样本中缺失。
通过标记启动子的可及性确定细胞类型身份
- 细胞类型注释(启动子可及性) 分析了20个经典肢芽标记
- Z值规范化的启动子可及性跨12个簇
- 明确的谱系分组 (指,近端,肌肉,外胚层,内皮,免疫,神经脊)
关键间质状态
- C1(指间质):高Hoxa13/Hoxd13 经典HOX13依赖的远端状态
- C11(过渡指) 甚至更高的Hox13可及性 更为坚定的远端身份
- C4(KO异常,KO专有) 高Msx1,Bmp2 Hoxa13/Hoxd13丧失 停滞的部分远端状态(非近端逆转)
- C3(近端间质) 高Meis1 确认近端身份
结论
- HOX13建立了远端指状染色质状态(C1)
- 丧失HOX13阻止了完整指状程序的激活
- 细胞转向异常状态(C4)
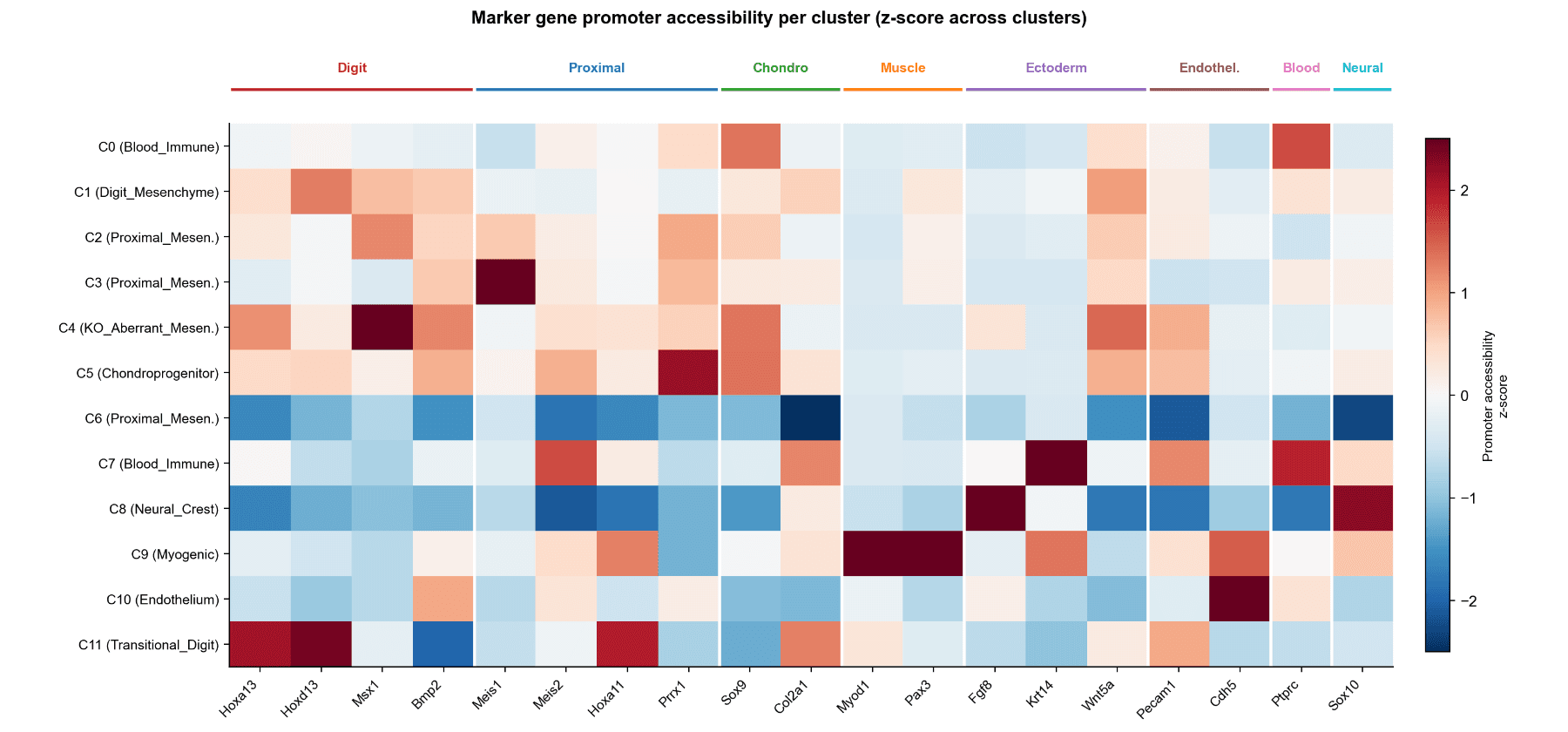
通过标记启动子的可及性确定细胞类型身份
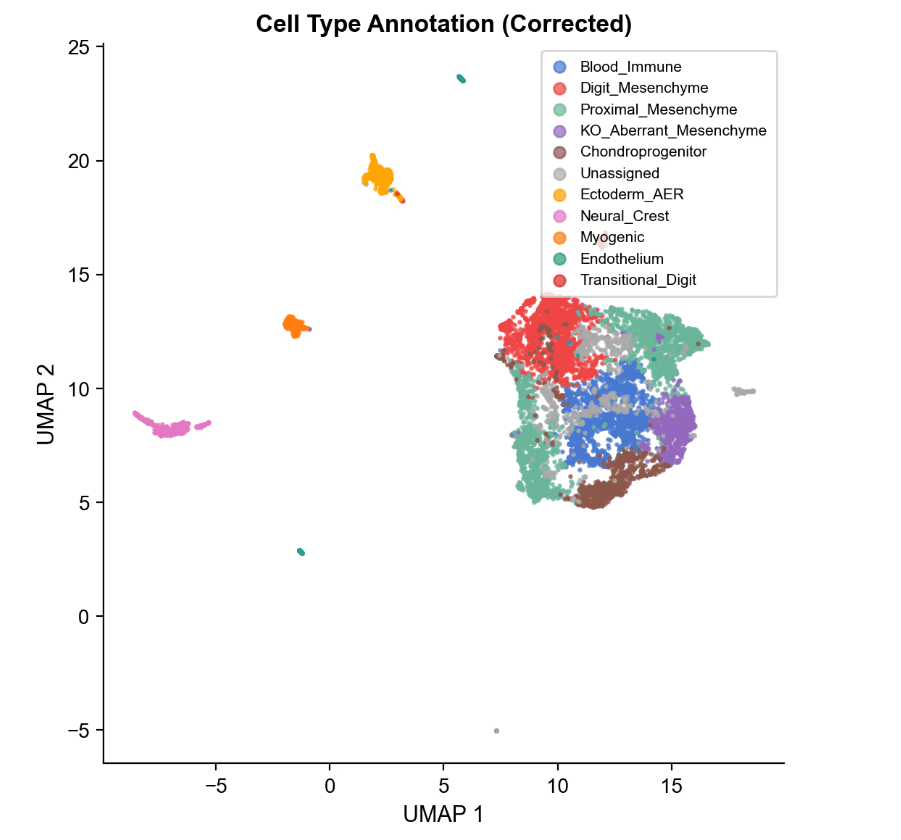
差异可及性 – 火山图
273,119个10-kb窗口的火山图。
- C1中有9,283个区域更为开放(蓝色,包括Hoxa13和Hoxd13位点)。
- C4中有5,357个区域更为开放(红色,包括Bmp2位点)。近2:1的比例显示HOX13丧失主要阻止了正确位点的开放。
-> C1和C4之间的差异染色质可及性揭示了HOX13依赖的调控景观:
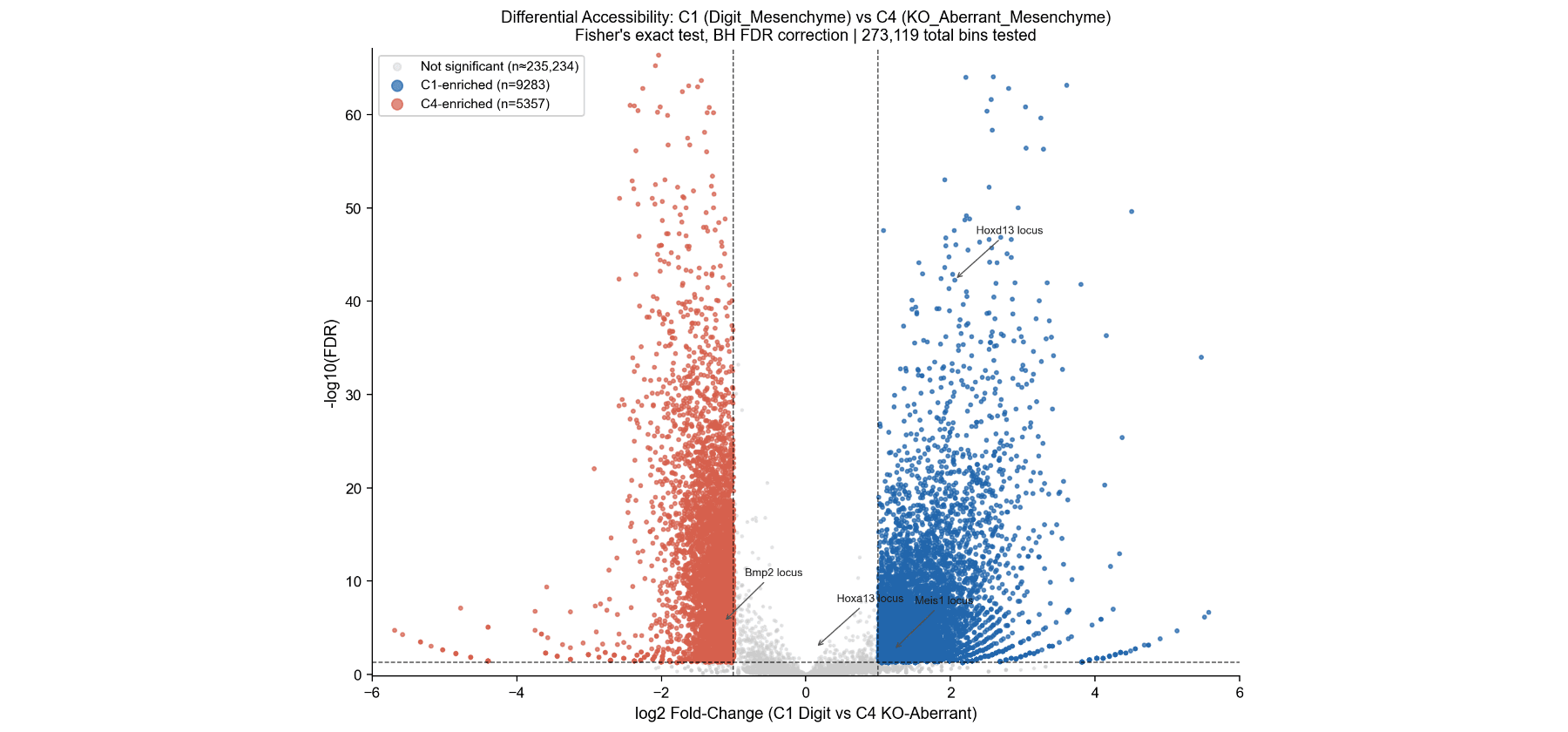
基因组浏览器轨迹
三个代表性位点。
左 & 中:在Hoxa和Hoxd簇上的强C1特异性(黄色)峰值。
右:在chr5:45.5–48.0 Mb的多个C4特异性(紫色)峰值(异常开放)。
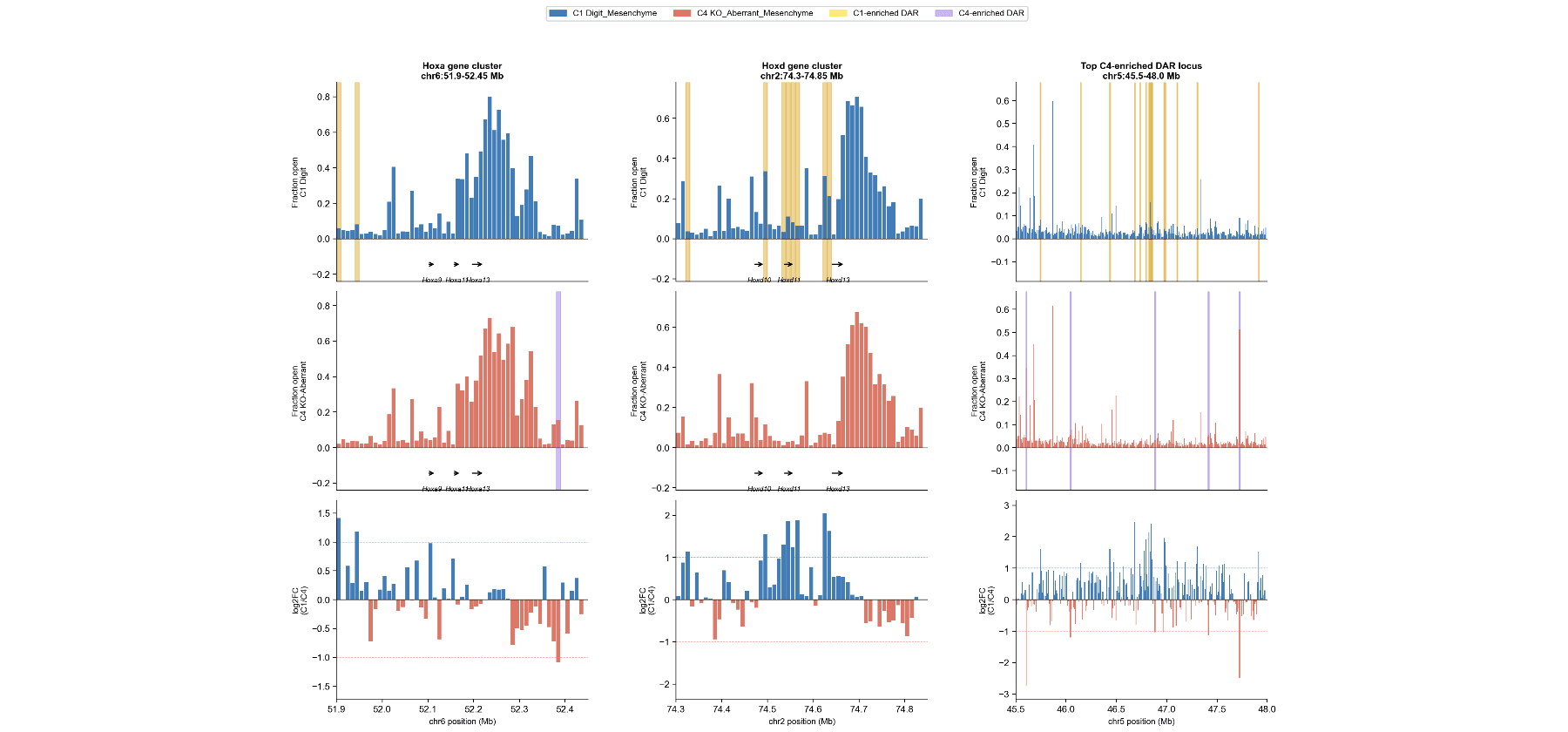
HOMER转录因子基序富集
- C1 DARs: 8个显著的基序 (q < 0.05),其中5个为同源框/TALE (最高: Tgif2, q = 0.0003)。
- C4 DARs: 0个显著基序 (最佳 q = 0.99)。
HOX13与TALE伙伴(TGIF1/2)合作以开放指状增强子;KO中的异常开放是无编程性质的。
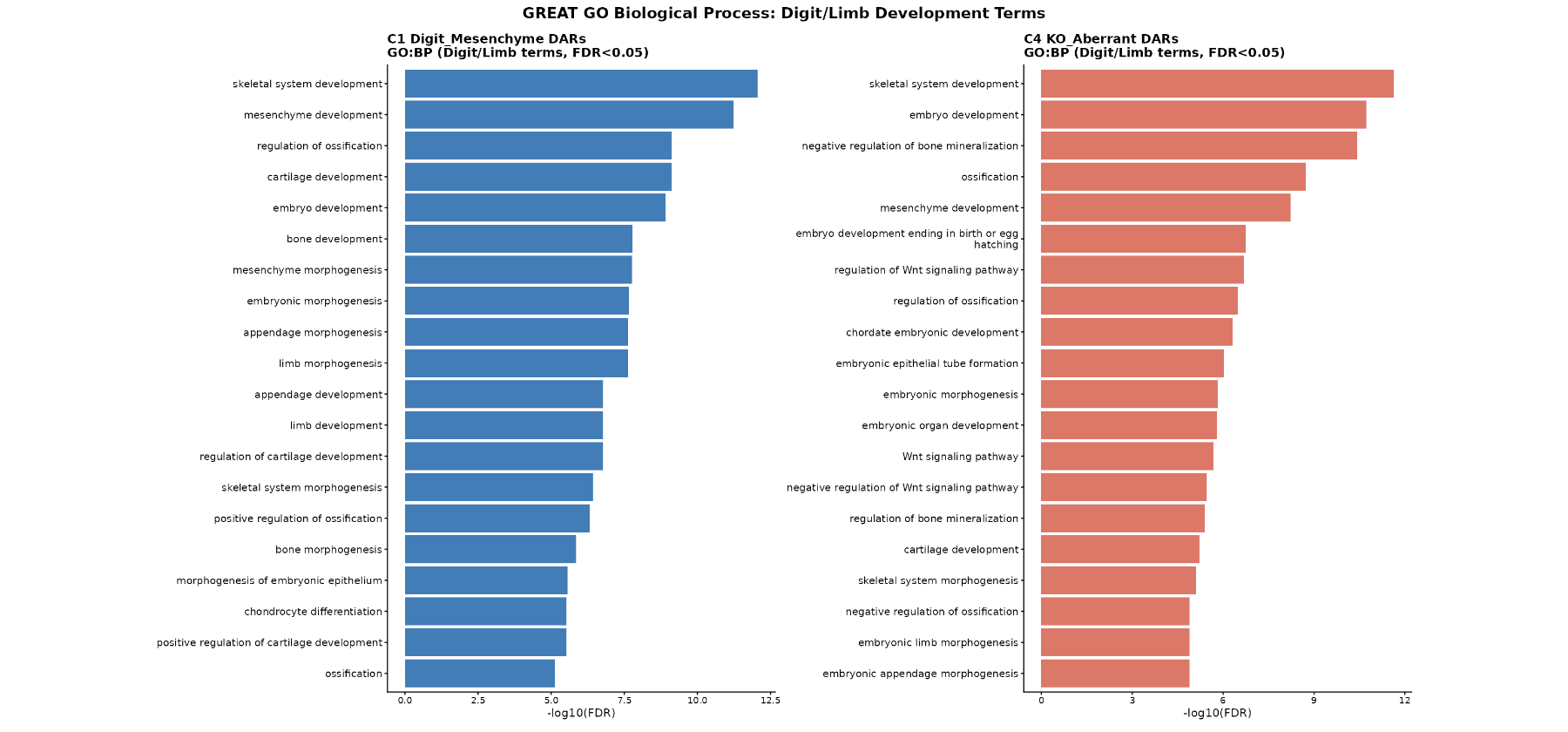
GREAT GO生物过程富集
DAR集 | 显著GO:BP (FDR < 0.05) | 关键指/肢术语 |
|---|---|---|
C1 | 1,709 | 骨骼系统发育 (FDR = 8.8e-13),间质发育 (FDR = 5.8e-12),附属物/肢体形态发生 (FDR = 2.4e-8),软骨发育,骨化调节 |
C4 | 1,917 | 骨骼系统发育,骨矿化负调节 (FDR = 3.7e-11,倍数 = 3.78),Wnt信号通路调节 (FDR = 2.1e-7),胚胎肢体形态发生 |