
数据集概览
GSE201610:来自空间对象识别(SOR)训练实验的小鼠大脑的10x Genomics Visium空间转录组学
属性 | 详情 |
|---|---|
生物体 | 小鼠 (mouse) |
组织 | 大脑矢状切片 |
平台 | 10x Visium + Illumina NovaSeq 6000 |
样本 | 共6个:3个家笼控制(HC1–HC3)+ 3个SOR训练(SOR1–SOR3) |
斑点/样本 | 每张切片2,550–2,936个 |
基因 | 共32,285个 |
GEO登录号 | GSE201610 |
细胞类型 | 未预先注释;通过无监督分析识别 |
已完成的分析
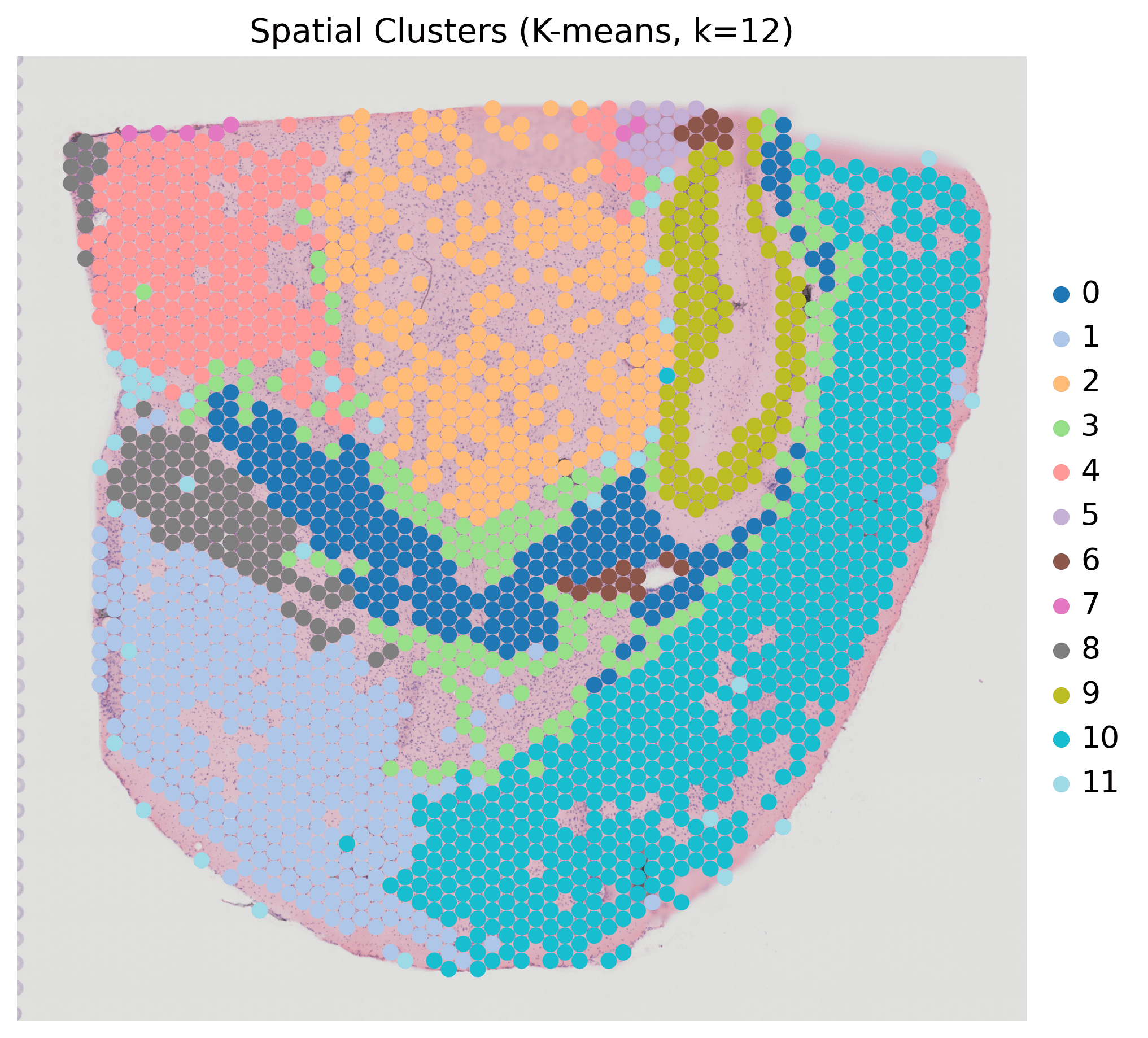
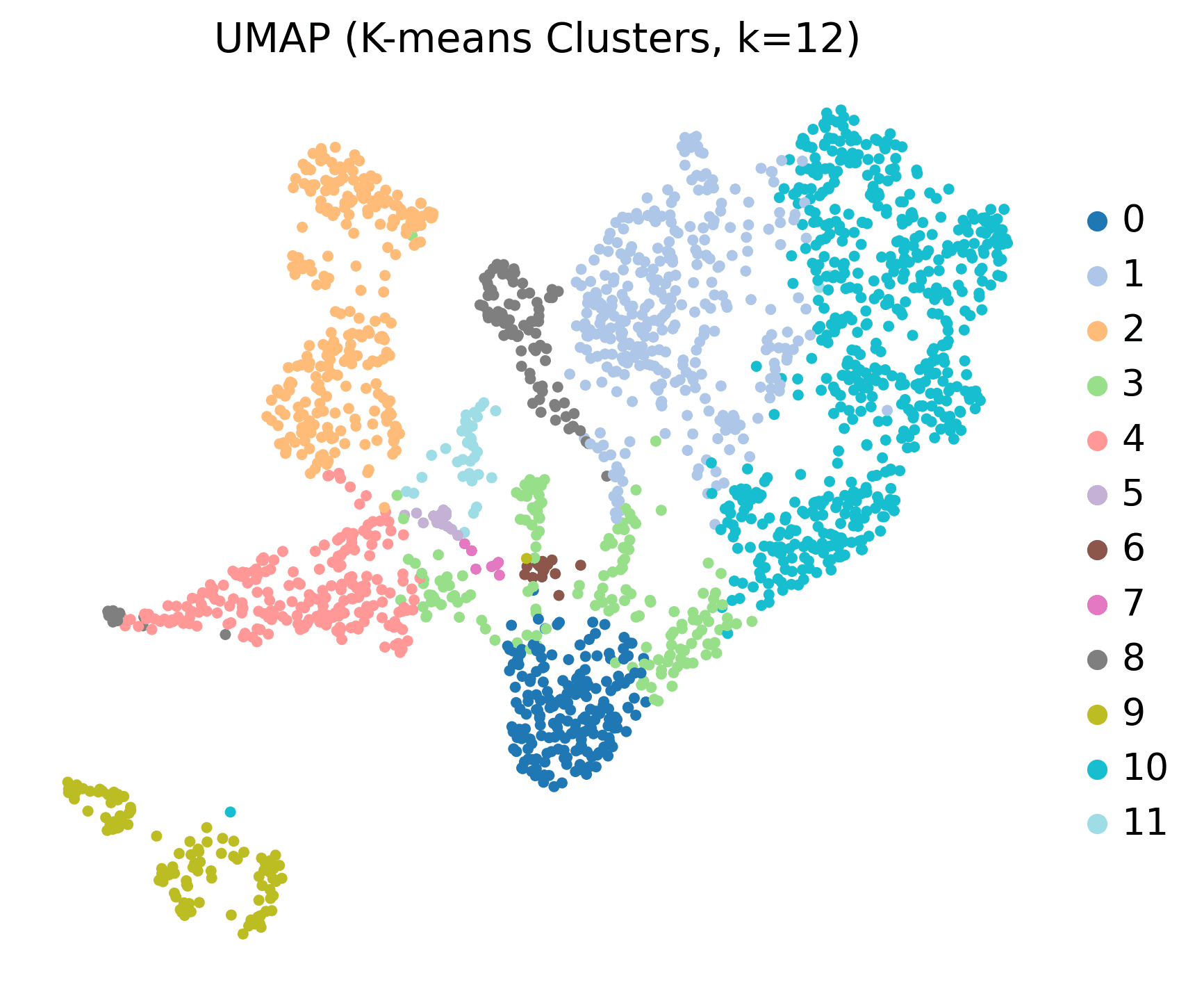
无监督空间聚类(单样本:HC1)
方法:PCA + K-means聚类(k=12)
输出结果:具有解剖学定义区域的12个空间聚类
关键发现:成功识别寡突胶质细胞、神经元、脉络丛、室管膜细胞和基质区域与经典标志基因
全样本聚类(所有6个样本)
方法:质量筛选 → SCTransform → Louvain聚类(分辨率0.5)
保留:10,839个斑点(16,451个总数的66%)
输出结果:18个解剖学一致的空间区域
标志基因:在各区域中显着差异表达的16,743个基因

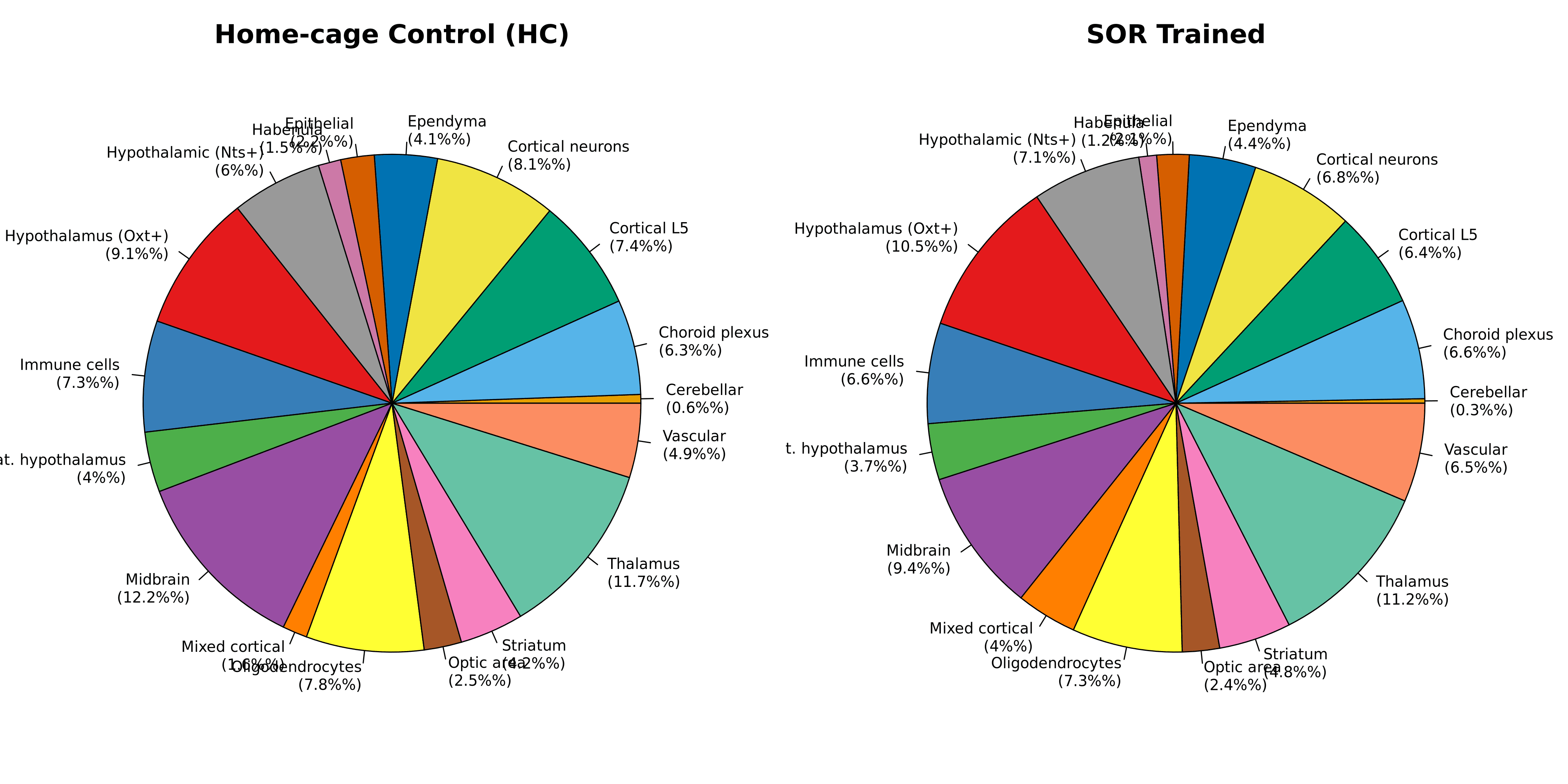
条件比较:HC vs SOR(比例分析)
比较:家笼控制(n=3)对比SOR训练(n=3)
关键发现:
丘脑:11.7% (HC) 对比11.2% (SOR) — 变化极小
中脑:12.2% (HC) 对比9.4% (SOR) — SOR减少2.8%(多巴胺能/5-羟色胺能回路)
下丘脑(Oxt+):9.1% (HC) 对比10.5% (SOR) — SOR增加1.4%
混合皮质:1.6% (HC) 对比4.0% (SOR) — SOR增加2.4%(潜在学习的可塑性)
总体而言:解剖结构在条件之间高度保守
脑膜/血管空间定位(HC1对比SOR1)
使用的标志:Col1a2, Dcn, Vtn, Col1a1, Col3a1
HC1结果:83个脑膜斑点(组织的3.12%),集中于周围
SOR1结果:71个脑膜斑点(组织的2.78%)
关键发现:脑膜/血管隔室在条件之间结构上保留

关键生物学见解
完整的大脑结构:无监督聚类忠实再现已知的小鼠大脑解剖结构,并清晰划分主要结构(丘脑、中脑、皮质、下丘脑、白质、脉络丛)
训练诱导的组成变化:
SOR中的中脑减少表明多巴胺能/5-羟色胺能回路可能调节
SOR中的皮质增加可能反映学习相关的可塑性
总体效应量适度(绝对变化小于3%),需要更大队列进行统计验证
保留的基质/血管隔室:脑膜和血管结构在HC和SOR条件下保持结构相似
推荐的后续分析
基于参考的去卷积:应用RCTD或Cell2location结合Allen脑图谱scRNA-seq以获得更高的细胞类型分辨率
统计测试:正式的组成数据分析(ALDEx2, scCODA)用于差异丰度
空间差异表达:识别在特定脑区内具有条件依赖表达的基因
通路富集:在显示组成变化的区域中表征功能程序
更大的样本量:目前每组n=3限制统计能力;建议n≥5以获得稳健结论